Postagem relacionada
Analise Proteínas de Membrana com XL-MS: Guia de Fluxo de Trabalho Passo a Passo
2026-02-20Analisar Proteínas de Membrana com XL-MS é uma das formas mais práticas de transformar interações de membrana "difíceis de ver" em evidências mensuráveis. A Longlight Technology utiliza reticulação química acoplada à espectrometria de massa (XL-MS) para ajudar pesquisadores a mapear interações proteína-proteína (PPIs), capturar contatos fracos ou de curta duração e passar de hipóteses para modelos estruturais defensáveis — sem forçar fluxos de trabalho especiais de marcação química.
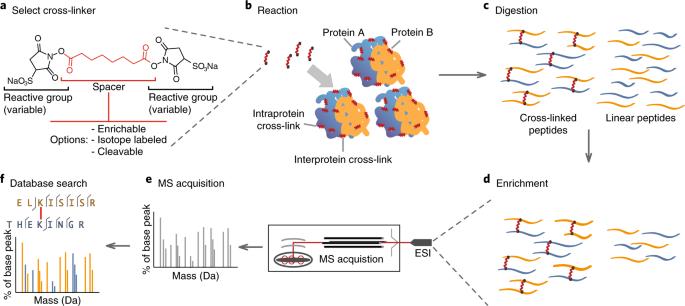
Espectrometria de massa de reticulação: métodos e aplicações em estruturas, moleculares e sistemas
O que é XL-MS? O que são proteínas de membrana?
XL-MS e proteínas de membrana são duas ideias que frequentemente aparecem juntas na biologia estrutural e na descoberta de medicamentos. Aqui está uma explicação clara e amigável para iniciantes.
O que é XL-MS?
XL-MS significa espectrometria de massa de reticulação (frequentemente escrita como reticulação química acoplada a espectrometria de massa).
É um método usado para estudar interações e formas de proteína, fazendo duas coisas:
Reticulação (XL): "Congele" as partes próximas no lugar
Um reticulador químico age como uma pequena "ponte" molecular. Se dois sítios de aminoácidos estiverem próximos o suficiente no espaço real (a uma curta distância), o reticulador pode conectá-los covalentemente.
Isso ajuda a preservar interações fracas ou de curta duração que podem se desfazer durante o manuseio normal da amostra.
Espectrometria de Massas (MS): Identificar as partes ligadas
Após a reticulação, as proteínas são digeridas em peptídeos. O espectrômetro de massa detecta pares de peptídeos cruzados e o software os mapeia de volta para proteínas.
Esses links fornecem pistas de distância (restrições espaciais), indicando quais regiões estavam próximas no complexo original.
O que o XL-MS te diz (na prática):
• Quais proteínas provavelmente interagem (rede de interação)
• Quais regiões se tocam (dicas de interface)
• Restrições estruturais que suportam modelos (frequentemente combinados com crio-EM ou raio-X)
O que são proteínas de membrana?
Proteínas de membrana são proteínas que estão embutidas ou ligadas a uma membrana celular (ou membranas dentro das células, como o RE, mitocôndrias ou membranas bacterianas).
Elas são críticas porque as membranas controlam o transporte e a sinalização, e as proteínas membranares frequentemente atuam como "guardiãs" ou "antenas" para a célula.
Principais Tipos
• Proteínas integrais de membrana: fisicamente embutidas na membrana
• Muitas atravessam a membrana uma ou várias vezes (frequentemente chamadas de proteínas transmembranares)
• Proteínas periféricas de membrana: ligadas à superfície da membrana (frequentemente por meio de outras proteínas ou lipídios)
Por que as proteínas de membrana são importantes
• Eles estão envolvidos em:
• Transporte (canais, bombas, transportadores)
• Sinalização celular (receptores como GPCRs)
• Conversão de energia (complexos de cadeia respiratória)
• Reconhecimento e adesão celular
Por que eles são "difíceis"
Proteínas de membrana são desafiadoras de estudar porque:
• Eles ficam em ambiente lipídico
• Podem ficar instáveis quando removidos da membrana
• Frequentemente formam complexos dinâmicos que mudam de estado
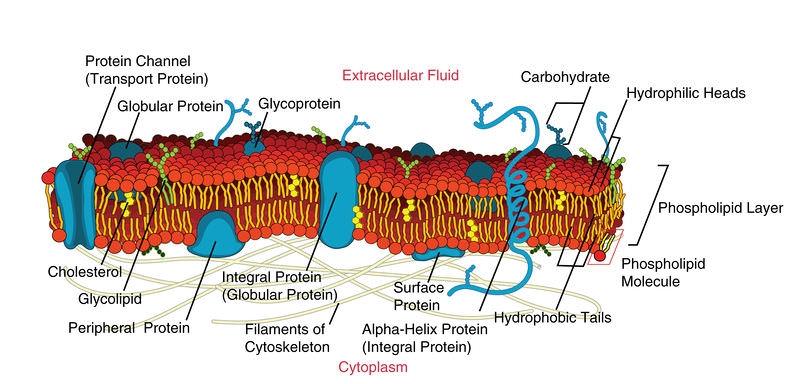
Proteínas de membrana - Biologia LibreTexts
Por que as proteínas de membrana precisam a Estratégia Diferente
Proteínas de membrana frequentemente ficam em ambientes dinâmicos e lotados. Suas interfaces principais podem ser transitórias, e muitos complexos tornam-se instáveis uma vez removidos da membrana. Por isso, métodos clássicos de interação podem deixar de perceber contatos críticos ou simplificar demais o que está acontecendo.
O Analyze Membrane Proteins com XL-MS funciona porque ele "congela" regiões próximas usando agentes de reticulação. Esses reagentes podem conectar covalentemente duas ou mais proteínas interagindo dentro de uma janela de distância definida. Uma vez que a interação está consolidada, a espectrometria de massa pode ler peptídeos cruzados e apontar para possíveis pontos de contato. Operacionalmente, as evidências de interação permanecem rastreáveis mesmo quando os complexos são fracos.
• Assegura interações de curta duração frequentemente perdidas durante a purificação
• Evita a marcação química, simplificando decisões iniciais
• Possibilita a reticulação intracelular para preservar a proximidade nativa
Passo 1: Especifique a questão biológica e a justificativa da distância
Decida o que você quer aprender antes de começar. Você está confirmando um parceiro suspeito? Comparando a ligação entre mutantes e selvagem? Mapeando uma interface para suportar um modelo? Uma pergunta clara ajuda você a escolher condições, controles e saídas de dados.
XL-MS é informado por distância. Agentes de reticulação conectam resíduos que estão próximos no espaço, não necessariamente adjacentes em sequência. Para proteínas de membrana, essa lógica de distância é valiosa porque pode revelar como as hélices se empacotam, como os laços citosólicos entram em contato com parceiros ou como os oligômeros se formam.
Uma forma amigável para iniciantes de estruturar seu plano é definir três saídas:
• Presença de Interação: A entra em contato com B?
• Topologia de Interação: quais regiões de A se conectam com quais regiões de B?
• Evidência do Local: quais pares de peptídeos apoiam a rede de interação?
Analisar Proteínas de Membrana com XL-MS fica muito mais fluido quando você pré-decide quais dessas opções precisa para sua próxima decisão (modelagem estrutural, validação de alvos ou estudo de mecanismos).
Passo 2: Escolha a Abordagem de Reticulação que se encaixa no contexto da membrana
Proteínas de membrana são sensíveis a detergentes, miméticos lipídicos e composição tampão. O objetivo é manter um estado que se assemelhe ao complexo funcional o mais próximo possível e, em seguida, fazer a ligação cruzada no momento certo.
Na Longlight Technology, os clientes podem enviar amostras já reticuladas ou nos contatar para desenvolver um plano de reticulação e depois enviar amostras. Essa flexibilidade é importante para alvos de membrana porque um projeto pode exigir reticulação em solução, enquanto outro se beneficia de condições mais nativas ou até mesmo de reticulação intracelular.
✔ Alta taxa de transferência e rápida velocidade de análise podem encurtar ciclos de iteração
✔ A reticulação intracelular pode reduzir artefatos provenientes de complexos de manuseio excessivo
✔ Nenhuma exigência especial de rotulagem mantém os primeiros experimentos acessíveis
Dica prática para iniciantes: planeje pelo menos um controle negativo (sem cruzamento, nem proteína parceira) e uma referência de "comportamento conhecido", se disponível. Os controles ajudam a distinguir sinais reais de proximidade do fundo.
Passo 3: A partir de proteínas entrecruzadas to Peptídeos Detectáveis
Após a reticulação, o fluxo de trabalho deve traduzir proteínas em uma mistura de peptídeos que ainda preserve as informações de ligação cruzada. É aí que muitos iniciantes se sentem perdidos, porque peptídeos reticulados são mais raros que peptídeos normais e podem ser mais difíceis de detectar.
Nosso fluxo de trabalho padrão de serviço cobre toda a cadeia:
• Digestão enzimática
• Enriquecimento peptídico
• Detecção por espectrometria de massa
• Análise de dados
• Entrega de relatórios experimentais
A ideia principal é simples: a digestão transforma as proteínas em peptídeos, o enriquecimento aumenta a visibilidade relativa das espécies entrecruzadas, e a espectrometria de massas mede as massas e fragmentos peptídicos para que o software possa atribuir pares de ligação cruzada.
Analisar Proteínas de Membrana com XL-MS é mais eficiente quando você trata a preparação da amostra como uma etapa de preservação de informações, e não apenas como um protocolo rotineiro. Os melhores resultados vêm de uma digestão estável e um enriquecimento cuidadoso para que os dados transmitam sinal suficiente para uma interpretação confiante.
Passo 4: Leitura de Espectrometria de Massa and Mapeamento de Rede de Interação
A espectrometria de massa faz mais do que "identificar proteínas". No XL-MS, ele identifica pares de peptídeos reticulados, que você pode interpretar como restrições espaciais. Quando você tem links de alta confiança suficientes, pode começar a representar redes de interação e inferir locais de ação — especialmente útil para conjuntos complexos de membrana.
É também aqui que o XL-MS se torna uma ponte para a biologia estrutural. Muitas equipes utilizam saídas XL-MS junto com crio-EM ou cristalografia de raios X. As evidências de ligação cruzada podem ajudar:
• Validar se um modelo estrutural é plausível
• Resolver orientações ambíguas de subunidades
• Suporte à colocação de domínio quando a densidade é limitada
Em outras palavras, Analisar Proteínas de Membrana com XL-MS pode levar você de "achamos que essas duas regiões interagem" para "temos evidências apoiadas pela distância que restringem o modelo."
Passo 5: Como to Leia tele Relatório and Transformar Dados em Próximos Experimentos
Um relatório só é valioso se orientar as decisões. Para iniciantes, a forma mais útil de ler resultados do XL-MS é procurar padrões, não apenas listas.
Comece com três perguntas:
✔ Os cruzamentos são reproduzíveis entre réplicas ou condições? A reprodutibilidade gera confiança.
✔ Os links se agrupam em regiões específicas? O agrupamento frequentemente aponta para interfaces reais.
✔ As condições do mutante/ligante alteram o padrão do link? Mudanças podem revelar mecanismos.
Depois, traduza as evidências para os próximos passos. Se os links suportarem uma interface específica, você pode projetar mutações pontuais para validação. Se os links sugerirem parceiros inesperados, você pode planejar confirmação ortogonal. Se links restringem um modelo, você pode avançar para o refinamento estrutural com maior confiança.
CTA: Se você quer Analisar Proteínas de Membrana com XL-MS, mas não tem certeza de como escolher condições ou controles, entre em contato com a Longlight Technology para desenvolver um plano de reticulação cruzada e receber um relatório completo de fluxo de trabalho — desde a digestão até a análise de dados. Obtenha um orçamento gratuito para começar seu projeto com um roteiro experimental claro e amigável para iniciantes.
Por que a Longlight Technology fou XL-MS and Além
Projetos de proteínas de membrana raramente vivem em uma única técnica. Normalmente, eles exigem uma mentalidade de plataforma: manuseio confiável das amostras, dados rigorosos e ferramentas que acelerem a iteração.
A Longlight Technology oferece suporte completo com soluções genômicas de ponta, instrumentos de laboratório avançados e reagentes e consumíveis de alta qualidade projetados para melhorar a eficiência e a precisão em laboratórios modernos. Além dos serviços XL-MS, apoiamos equipes de pesquisa com ferramentas de genômica e biologia molecular, incluindo instrumentos relacionados ao NGS, como sistemas de ultrassonagem focalizados, além de consumíveis e kits amplamente utilizados (géis de agarosa pré-moldados, kits de extração de ácidos nucleicos e kits de preparação de bibliotecas) para aplicações acadêmicas, clínicas e industriais.
Analisar Proteínas de Membrana com XL-MS não é apenas um método — é uma disciplina de fluxo de trabalho. Quando o fluxo de trabalho é estável, suas conclusões ficam mais claras, seus modelos mais defensáveis e seu próximo experimento fica mais fácil de projetar.